Ouranos et PostgreSQL.
Vers un stockage spatialisé des GCMs à haute résolution?
Steve Vissault
Chaire de recherche du Canada en biogéographie et écologie des métacommunautés
Mise en contexte...
Contexte de stage

Contexte de stage

Contexte de stage

Identification et réponse aux besoins
Objectif:
Stocker les sorties climatiques d'Ouranos (Fichier Matlab/HDF5) dans une base de données spatialisée pour l'Est de l'Amérique du Nord.
-Données mensuelles pour 3 variables climatiques: 570 240 grilles
-Données annuelles pour 19 biovariables climatiques: 300 960 grilles
Un stage en trois volets...
- Étude de faisabilité: Stockage et requêtes des grilles climatiques dans PostgreSQL (Automne 2014)
- Conceptualiser et réaliser la base de données spatialisée dans PostgreSQL (Hiver 2015)
- Créer un programme d'importation performant des fichiers HDFs (sorties climatiques d'Ouranos) vers la nouvelle base de données (Hiver 2015)
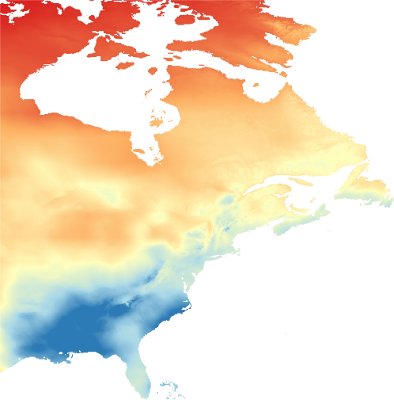
La couverture spatiale...
Qu'est-ce que PostgreSQL?
Qu'est-ce que PostgreSQL?
Un Système de Gestion de Base de données (SGBD) gratuit et openSource depuis 1989, composé de:
- Tables: Comprend des enregistrements
- Clés primaires: Assure des enregistrement uniques
- Jointures: Permet de créer des relations entre les tables
- Indexes: Permet une recherche plus rapide
- Intégrités référentielles: Garantie l'intégrité des données

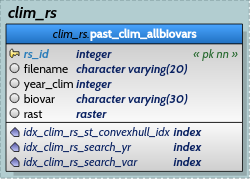
Volet 1: Conceptualisation de la base de données
Pour illustrer et comprendre, voici la base de données Ouranos:

- Pour créer des champs (colonnes) de type raster, nous avons besoins de l'extension PostGIS...
Qu'est-ce que PostGIS?
Qu'est ce que l'extension PostGIS ?
C'est une cartouche spatiale qui permet de stocker et de manipuler des objets spatiaux à l'intérieur de PostgreSQL.
Deux types d'objets spatiaux:
- Geometrique
- Polygones (Multi ou simple)
- Lignes
- Points (Multi ou simple)
- Raster/Grilles

Qu'elles sont les forces de PostGIS Raster?
Avantages:
- Indexation spatiale
- Stockage des grilles en héxadecimale (Diminue le poids des grilles)
- Posséder des fonctions permettant de traiter spatialement ces objets nativement à l'intérieur de la base de données (p.ex. Clip, Insersection/Interception, Aggregation spatiale et temporelle)
- Puissance de calcul (avec opérations matricielles)

Volet 2: Importer les grilles climatiques...
Des fichiers Matlab (HDF5) vers la base de données PostgreSQL...
L'importation se fait dans l'infrastructure de Colosse (Super-Calculateur de l'U-Laval).
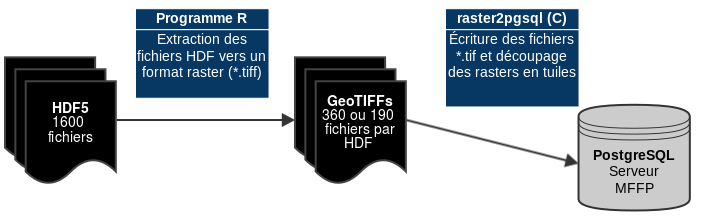
Le programme raster2pgsql découpe chaque raster climatique en tuile de 38 x 20 pixels.
Les grilles ne sont pas stockées en multibandes.
Des fichiers Matlab (HDF5) vers la base de données PostgreSQL...
Le programme et l'infrastructure permet de traiter jusqu'à 24 fichiers Matlab à la fois.
Vitesse de traitement d'un fichier HDF par le programme R/raster2pgsql:
- 12 minutes pour une importation des grilles mensuelles
- 30 minutes pour une importation des grilles annuelles
Durée totale de l'importation:
- 10-12 heures pour les grilles mensuelles
- 24 heures pour les grilles annnuelles
Sinon, ca ressemble à quoi dans la BD?
Quelques chiffres après importation...
Poids des indexes et tables:
| Relation | Poids (data) |
|---|---|
| clim_rs.fut_clim_vars | 358 GB (58 GB data) |
| clim_rs.fut_clim_biovars | 187 GB (30 GB data) |
| clim_rs.idx_spatial_mth | 6226 MB (index) |
| clim_rs.idx_mod_run_mth | 4983 MB (index) |
| clim_rs.rs_pkey | 4696 MB (index) |
| clim_rs.idx_spatial_bio | 3277 MB (index) |
| clim_rs.idx_mod_run_bio | 2622 MB (index) |
Table annuel avec 54 821 232 de lignes et mensuel avec 104 175 072 lignes
Comment interroger cette BD?
Le language SQL
On interroge une base de données en utilisant le language SQL (Stuctured Query Language).
Il permet la manipulation des données via des instructions (SELECT, INSERT, UPDATE, DELETE...).
Une requête simple:
SELECT rast, year_clim FROM clim_rs.past_clim_allbiovars
WHERE year_clim >= 1960 OR year_clim <=1970 AND biovar = 'annual_mean_temp';
Exemple de requête de manipulation spatiale sur raster
Aggregation temporelle:
SELECT ST_Union(rast,'MEAN') as tavg_6070, biovar FROM clim_rs.past_clim_allbiovars
WHERE year_clim >= 1960 OR year_clim <= 1970
GROUP BY biovar;
Liste des fonctions sur raster disponible sur postgis.net
Comment accéder à cette BD ?
Via pgAdmin3...
Via une librairie (driver) dans son language préféré
require(RPostgreSQL)
dbname <- "quicc_for_dev"
dbhost <- "localhost"
dbuser <- 'postgres'
dbport <- 5433
drv <- dbDriver("PostgreSQL")
# Connection à la base de données
con <- dbConnect(drv, host=dbhost, port=dbport, dbname=dbname,user=dbuser)
# Écriture de la requête
query_tmax_60 <- "
SELECT * FROM clim_rs.past_clim_allbiovars
WHERE biovar = 'annual_maximum_temp' AND year_clim = 1960"
# Éxécution de la requête
res <- dbGetQuery(con,query_tmax_60)
Via une librairie (driver) dans son language préféré
str(res)
## 'data.frame': 696 obs. of 5 variables:
## $ rs_id : int 2120847 2120870 2120878 2121336 2121307 2121308 2121309 2121310 2121311 2121312 ...
## $ filename : chr "1960_sg300_14.asc" "1960_sg300_14.asc" "1960_sg300_14.asc" "1960_sg300_14.asc" ...
## $ year_clim: int 1960 1960 1960 1960 1960 1960 1960 1960 1960 1960 ...
## $ biovar : chr "annual_maximum_temp" "annual_maximum_temp" "annual_maximum_temp" "annual_maximum_temp" ...
## $ rast : chr "01000001001975ADBD4F55B53F1975ADBD4F55B5BF33A5F5B7040058C09DA223B9FCBF524000000000000000000000000000000000AD10000030001E004A003"| __truncated__ "01000001001975ADBD4F55B53F1975ADBD4F55B5BF226E4E2503005EC0AF0D15E3FC1F524000000000000000000000000000000000AD10000030001E004A003"| __truncated__ "01000001001975ADBD4F55B53F1975ADBD4F55B5BF39622D3E050056C0AF0D15E3FC1F524000000000000000000000000000000000AD10000030001E004A003"| __truncated__ "01000001001975ADBD4F55B53F1975ADBD4F55B5BF282B86AB03005CC0967D5704FF3F404000000000000000000000000000000000AD10000030001E004A003"| __truncated__ ...
Visualiser dans R
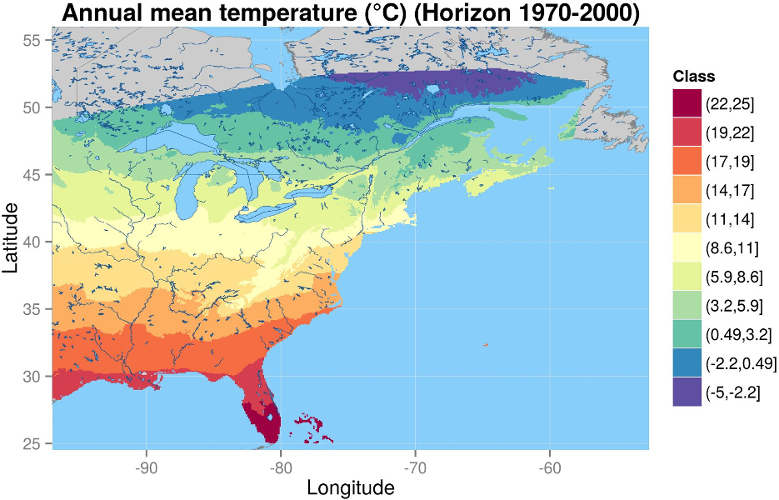
Les Geoserveurs...
Qu'est ce qu'un géoserveur ?
C'est un service (généralement) web fourni par un serveur et permettant à un client d'extraire des données spatialisées via les protocoles HTTP.
Il en éxiste trois sortes:
- Web Mapping Service (WMS): Pour visualiser des vecteurs ou des grilles comme des images cartographiques (JPEG , PNG , TIFF)
- Web Feature Service (WFS): Pour extraire des données géographiques dans diverses format (GeoJSON, KML, GML)
- Web Feature Service Transactional (WFS-T): Permet d'interagir directement avec les base de données (édition des objets spatiaux envoyé par le serveur).
La solution possible pour Ouranos
Selon le livre, Postgis in Action (Obe et Hsu, 2011), ce qui est recommandé pour vos besoins (soit 1. Visualisation et 2. Extraction) est MapServer, car il supporte toutes les extensions de PostGIS.

Un Exemple de Web Mapping Service (WMS) via R/Leaflet
require(rCharts)
require(knitr)
map1 = Leaflet$new()
map1$setView(c(52.731631, -70.156347), 4)
map1$tileLayer("http://{s}.tile.openstreetmap.se/hydda/base/{z}/{x}/{y}.png")
map1$set(width = 800, height = 550)
map1$save('maps/map1.html', cdn = TRUE)
Connecter le Web Mapping Service (WMS) avec PostgreSQL
Un exemple avec le Bas-Saint-Laurent...
query_climBSL <- "SELECT (ST_Intersection(rast,bsl.geom)).*, rs_id
FROM clim_rs.past_clim_allbiovars,
(SELECT geom FROM map_qc.regio_s WHERE res_nm_reg = 'Bas-Saint-Laurent') as bsl
WHERE year_clim=2010 AND biovar = 'annual_mean_temp'
AND ST_Intersects(rast,bsl.geom);"
Grille climatique de la température moyenne annuelle (°C) pour l'année 2010
(Bas-Saint-Laurent, interpolation par ANUSPLIN)